Luigi Ricciardi 1 , Rosa Mazzeo 2,*©, Angelo Raffaele Marcotrigiano 1 , Guglielmo Rainaldi 3 , Paolo Iovieno 4 , Vito Zonno 1 , Stefano Pavan 1© i Concetta Lotti 2,*
- 1 Departament de Ciències del Sòl, Plantes i Aliments, Unitat de Genètica Vegetal i Fitogenètica Universitat de Bari, Via Amendola 165/A, 70125 Bari, Itàlia; luigi.ricciardi@uniba.it (LR);angelo.marcotrigiano@uniba.it (BRAÇ); vito.zonno@uniba.it (VZ); stefano.pavan@uniba.it (SP)
- 2 Departament de Ciències de l'Agricultura, l'Alimentació i el Medi Ambient, Universitat de Foggia, Via Napoli 25, 71122 Foggia, Itàlia
- 3 Departament de Biociències, Biotecnologies i Biofarmacèutics, Universitat de Bari, Via Orabona 4, 70125 Bari, Itàlia; guglielmo.rainaldi@uniba.it
- 4 Departament de Tecnologies Energètiques, Divisió de Bioenergia, Biorefineria i Química Verda, Centre de Recerca ENEA Trisaia, SS 106 Ionica, km 419+500, 75026 Rotondella (MT), Itàlia; paolo.iovieno@enea.it
* Correspondència: rosa.mazzeo@unifg.it (RM); concetta.lotti@unifg.it (CL)
Resum:
Ceba (Allium cepa L.) és el segon cultiu d'hortalisses més important del món i és molt apreciat pels seus beneficis per a la salut. Malgrat la seva important importància econòmica i el seu valor com a aliment funcional, la ceba ha estat poc investigada pel que fa a la seva diversitat genètica. Aquí, vam estudiar la variació genètica de la "ceba vermella Acquaviva" (ARO), una raça local amb una història centenària de cultiu en una petita ciutat de la província de Bari (Apulia, sud d'Itàlia). Es va utilitzar un conjunt d'11 marcadors microsatèl·lits per explorar la variació genètica en una col·lecció de germoplasma formada per 13 poblacions ARO i tres tipus comercials comuns. Les anàlisis de l'estructura genètica amb mètodes paramètrics i no paramètrics van posar de manifest que l'ARO representa un conjunt de gens ben definit, clarament diferent de les races locals Tropea i Montoro amb les quals sovint s'equivoca. Per tal de proporcionar una descripció dels bulbs, habitualment utilitzats per al consum fresc, es va avaluar el contingut en sòlids solubles i la picor, mostrant una dolçor més alta en l'ARO respecte a les dues varietats autòctones esmentades anteriorment. En conjunt, el present estudi és útil per a la futura valorització de l'ARO, que es podria potenciar mitjançant segells de qualitat que podrien contribuir a limitar els fraus comercials i millorar els ingressos dels petits productors.
introducció
El gènere Allium inclou unes 750 espècies [1], entre les quals la ceba (Allium cepa L., 2n = 2x =16) és una de les més esteses. A. cepa té un cicle biennal i un comportament reproductiu de superació. Actualment, la producció mundial de ceba (97.9 Mt) la converteix en el segon cultiu d'hortalisses més important després del tomàquet [2]. Des de temps antics, els bulbs de ceba s'han utilitzat tant com a aliment com en aplicacions medicinals populars. De fet, els antics egipcis ja van informar de diverses fórmules terapèutiques basades en l'ús d'all i ceba en un papir mèdic del 1550 aC, el Codex Ebers [3].
Aquesta verdura versàtil i saludable es consumeix crua, fresca o com a producte processat, i s'utilitza per millorar el gust de molts plats. Diversos estudis recents afirmen que el consum de ceba pot reduir el risc de malalties cardiovasculars [4,5], obesitat [6], diabetis [7] i diverses formes de càncer [8-10]. Les propietats de la salut de la ceba sovint s'atribueixen a nivells elevats de dues classes de compostos nutracèutics: flavonoides i sulfòxids d'alk(en)il cisteïna (ACSO). La primera classe inclou flavonols i antocians. La quercetina és el principal flavonol detectable, conegut per les seves fortes propietats antioxidants i antiinflamatòries en l'eliminació de radicals lliures i la unió d'ions de metalls de transició. [11]; mentre que les antocianines confereixen color vermell/violet a algunes varietats de ceba. Pel que fa als ACSO, el més abundant és la isoalliïna [(+)-trans-S-1-propenil-L-cisteïna sulfòxid] [12], un aminoàcid de sofre no volàtil i no proteinogènic emmagatzemat a les cèl·lules, que és indirectament responsable de l'aroma i el gust picant de les cebes. [13]. Després de la ruptura del teixit, l'enzim aliinasa escinda l'isoalliina per produir una sèrie de compostos volàtils (piruvat, amoníac, tiosulfonats i S-òxid propanetial) que indueixen llàgrimes i provoquen olor desagradable (aciditat). [14]. La picor de la ceba sovint es mesura com la quantitat, per gram de pes fresc, d'àcid pirúvic generat per hidròlisi [15,16].
Als països de la conca mediterrània, proposat com un dels centres secundaris de diversitat de A. cepa [17,18], els bulbs de ceba mostren una gran variabilitat en forma, mida, color, matèria seca i picor [19-22]. A més, la fertilització a base de sofre, les pràctiques agronòmiques, el tipus de sòl, les condicions climàtiques i el genotip de cultivars o varietats autòctones poden influir en la qualitat del bulb, conferint uns valors organolèptics i nutricionals peculiars. [23-27]. A Itàlia, malgrat l'àmplia disponibilitat de germoplasma de ceba, només algunes varietats de ceba sovint se sotmeten a estudis científics i es caracteritzen adequadament. [28,29].
La caracterització genètica i fenotípica exhaustiva de l'agrobiodiversitat és crucial per assegurar la conservació adequada dels recursos genètics vegetals i promoure l'ús de genotips específics en la cadena de valor. [30-32]. Sovint s'han triat marcadors de repetició de seqüència simple (SSR) per al mapeig [33-35], empremtes dactilars d'ADN i discriminació de cultivars [36-38], i una estimació fiable de la variabilitat genètica dins i entre les races autòctones [39-42], ja que són locus específics, multial·lèlics, heretats de manera codominant, altament reproduïbles i aptes per al genotipat automatitzat.
En el present estudi, hem centrat la nostra atenció en una raça tradicional d'Apulia, la "ceba vermella Acquaviva" (ARO), que es conrea segons mètodes d'agricultura ecològica en una petita zona de la ciutat d'Acquaviva delle Fonti, a la província de Bari. (Puglia, sud d'Itàlia). Els bulbs d'aquesta raça local són grans i aplanats i de color vermell i s'utilitzen àmpliament en receptes locals. Tot i que l'ARO va obtenir el segell de qualitat "Slow Food Presidium", la seva producció es podria promoure i protegir encara més amb marques de qualitat de la Unió Europea com la indicació geogràfica protegida (IGP) i la denominació d'origen protegida (POD), ja que poden contribuir a limitar la fraus comercials i millorar els ingressos dels petits propietaris. Aquí, els marcadors moleculars SSR es van utilitzar com a eines poderoses per avaluar la variació genètica entre les poblacions d'ARO i per discriminar aquesta raça local d'altres dues races de ceba vermella del sud d'Itàlia. A més, hem estimat el contingut de sòlid soluble i picant per avaluar el sabor ARO en relació amb la demanda del mercat.
Resultats
Establiment de la Col·lecció de Germoplasma de Ceba Roja Acquaviva i Caracterització Morfològica
Les llavors de 13 poblacions de la raça local ARO, donades pels agricultors en el marc del projecte BiodiverSO Apulia Region, es van utilitzar per establir una col·lecció de germoplasma ARO.
Els descriptors morfològics, relacionats amb el bulb, la pell i la carn, es van recollir en germoplasma ARO i en tres races de ceba, dues pertanyents a la raça local "Tropea red onion" (TRO) i una a la varietat local "Montoro copper onion" (MCO) (Figura 1). Tots els bulbs ARO eren plans i es caracteritzaven per la pell externa vermella i la carn amb diferents tons de vermell. En canvi, la carn dels bulbs TRO era completament vermella, mentre que la carn dels bulbs MCO estava mal pigmentada (taula S1). L'anàlisi bioquímica va permetre avaluar el contingut de sòlid soluble i la picor. Tal com s'informa a la taula 1, els valors mitjans del contingut sòlid soluble dels bulbs a les poblacions ARO van ser de 7.60 i van oscil·lar entre 6.00 (ARO12) i 9.50 ° Brix (ARO11 i ARO13). Aquest valor era superior a l'estimat per a les races locals TRO i MCO (4.25 i 6.00° Brix, respectivament).

Taula 1. Contingut soluble en sòlids i valors de punxència avaluats a les poblacions "Acquaviva Red Onion" (ARO), "Tropea Red Onion" (TRO) i "Montoro Copper Onion" (MCO) *.
| CODE | Contingut sòlid soluble (Brix) | punxència (pmolg-1 FW) | ||
| Significar | CV y (%) | Significar | CV y (%) | |
| ARO1 | 6.25 D * | 5.65 | 5.84 ab * | 23.78 |
| ARO2 | 7.25 DC | 4.87 | 6.51 01:00 | 22.98 |
| ARO3 | 7.50 aC | 9.42 | 5.28 ab | 22.88 |
| ARO4 | 7.50 aC | 0.00 | 6.97 01:00 | 3.74 |
| ARO 5 | 7.50 aC | 0.00 | 6.80 01:00 | 9.68 |
| ARO6 | 6.25 D | 5.65 | 4.51 ab | 39.18 |
| ARO7 | 7.25 DC | 4.87 | 5.25 ab | 15.44 |
| ARO8 | 9.00 AB | 0.00 | 7.04 01:00 | 3.49 |
| ARO9 | 8.25 ABC | 4.28 | 6.84 01:00 | 0.15 |
| ARO10 | 7.00 DC | 0.00 | 5.94 ab | 6.57 |
| ARO11 | El 9.50 | 7.44 | 5.54 ab | 16.43 |
| ARO12 | 6.00 D | 0.00 | 4.91 ab | 9.70 |
| ARO13 | El 9.50 | 7.44 | 6.63 01:00 | 24.93 |
| MCO | 6.00 D | 0.00 | 4.18 ab | 2.66 |
| TRO1 | 4.25 I | 8.31 | b 2.80 | 2.10 |
| TRO2 | 4.25 I | 8.31 | 4.28 ab | 4.79 |
* Els mitjans amb les mateixes lletres en majúscules o minúscules no són estadísticament diferents a 0.01P o 0.05P, respectivament (prova de SNK). y Coeficient de variació.
El valor mitjà de la picor ARO, avaluat mitjançant el contingut d'àcid pirúvic, va ser de 6.00, oscil·la entre 4.51 pmol g.-1 FW (ARO6) a 7.04 (ARO8). Aquest valor era superior a l'estimat en les races locals TRO i MCO (3.54 pmol g-1 FW i 4.18 pmol g-1 FW, respectivament).
Polimorfisme SSR i relacions genètiques entre accessions
En el present estudi, 11 de les 37 combinacions d'encebadors SSR provades van proporcionar polimorfismes d'un sol locus, és a dir, produint com a màxim dos productes d'amplificació en un sol individu. En total, es van detectar 55 al·lels en 320 individus amb un nombre d'al·lels per locus que va de 2 (ACM147 i ACM 504) a 11 (ACM132) i un valor mitjà de 5 al·lels (taula). 2). En poblacions individuals, el nombre d'al·lels (Na) oscil·lava entre 1.94 (ACM147 i ACM504) i 5.38 (ACM132), mentre que el nombre efectiu d'al·lels (Ne) oscil·lava entre 1.41 (ACM152) i 2.82 (ACM449). Discrepàncies entre els valors de Na i Ne es deuen a la presència d'al·lels amb baixa freqüència a les poblacions i al predomini d'uns pocs al·lels. El valor d'heterozigositat (Ho) més alt observat es va destacar per a ACM138 i ACM449 (0.62), mentre que el més baix es va associar amb ACM152 (0.25). L'heterozigositat esperada (He), que correspon a l'expectativa teòrica en una població panmíctica, va oscil·lar entre 0.37 (ACM504) i 0.61 (ACM132, ACM138 i ACM449). L'índex de fixació de Wright (Fis), mostrava valors propers a zero (mitjana 0.05) per a tots els marcadors, indicant valors similars entre els nivells d'heterozigositat observats i esperats, com s'esperava per a una espècie de creuament. L'eficiència del marcador SSR individual en l'empremta genètica es va estimar mitjançant l'índex de contingut d'informació polimòrfica (PIC), amb un valor mitjà de 0.48 i oscil·lava entre 0.33 (ACM504) i 0.67 (ACM132). Un altre índex d'eficiència, l'Índex d'Informació de Shannon (I), mostrava un valor mitjà de 0.84 i els valors assumits oscil·laven entre 0.45 (ACM152) i 1.20 (ACM132).
Taula 2. Característiques de polimorfisme dels 11 marcadors SSR utilitzats per estimar la diversitat genètica en poblacions ARO, TRO i MCO. Nombre total d'al·lels (Na), rang de mida de banda i índex de contingut d'informació polimòrfica (PIC) Consulteu el conjunt total de 320 individus genotipats en aquest estudi. Nombre d'al·lels (Na), nombre d'al·lels efectius (Ne), heterozigositat observada (Ho), heterozigositat esperada (He), índex de fixació (Fis), i l'índex d'informació de Shannon (I) es refereixen a valors mitjans calculats a partir de 16 poblacions, cadascuna composta per 20 individus.
| Locus. | Na total | Interval de mida (pb) | PIC | Significar | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | -0.02 |
| ACM147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | -0.01 |
| ACM152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | -0.06 |
| ACM446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | -0.03 |
| ACM463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| Significar | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
Entre les poblacions, ARO3, ARO6, ARO8, ARO10, TRO1 i MCO van mostrar un alt nivell de variació genètica (Ho > 0.5, 7), mentre que la diversitat més baixa es va observar a la població ARO0.27 (Ho = 2, XNUMX) (Taula complementària SXNUMX). En general, totes les accessions mostraven Fis valors propers a zero (Fis valor mitjà = 0.054), com s'esperava en condicions d'aparellament aleatori.
Anàlisi de la variància molecular i l'estructura genètica
AMOVA va calcular la partició jeràrquica de la variació genètica entre i dins de les poblacions. Els resultats van posar de manifest una fracció considerable de la variació genètica dins de les poblacions (87%). La variació entre poblacions, un 13%, va ser molt significativa (P < 0.001) (Taula 3). Els valors per parelles del paràmetre Fpt, un anàleg de l'índex de fixació Fst de Wright, que van des de 0.002 (ARO2/ARO10) fins a 0.468 (ARO7/TRO2), van ser significatius (P <0.05), excepte per a nou comparacions per parelles (taula complementària S3).
Taula 3. Anàlisi de la variància molecular de 320 genotips de 16 poblacions de Allium cepa L.
| font | df | Suma de places | Estimació de la variància | Desacord (%) | Fpt | P |
| Entre poblacions | 15 | 458.63 | 1.16 | 13% | ||
| Dins de les poblacions | 304 | 2272.99 | 7.50 | 87% | 0.134 | 0.001 |
| Total | 319 | 2731.62 | 8.66 |
Investigació de l'estructura genètica en el A. cepa La col·lecció genotipada en aquest estudi es va realitzar mitjançant l'anàlisi de clúster basat en models de barreja implementada al programari STRUCTURE. El mètode d'Evanno AK va suggerir la subdivisió en dos grups (K = 2) com el més informatiu per al nostre conjunt de dades,amb the next pe més altak a K = 5 (Regla complementària S1). La per K = 2, ahpopulations wabans el culigned a onif els dos clústers amb un coeficient de rnernbertoip (q) > 0.7. Com shown dins Figura 2a, el primer clúster (anomenat S1) incloïa MCO i totes les poblacions ARO, mentre que el clúster S2 agrupava les dues poblacions TRO. A K = 5, proporcionant una descripció més profunda del conjunt de dades (figura 2b), el 75% de les accessions es van assignar a un dels cinc clústers. Es va confirmar la separació entre ARO (S1) i TRO (S2), tot i que algunes poblacions d'ARO es van barrejar (q <0.7, 3) o agrupades per separat en els dos nous clústers S4 i S7 (ARO12 i ARO5, respectivament). Curiosament, el tipus comercial MCO va formar un grup diferent (SXNUMX) separat de la ceba vermella d'Apulia.
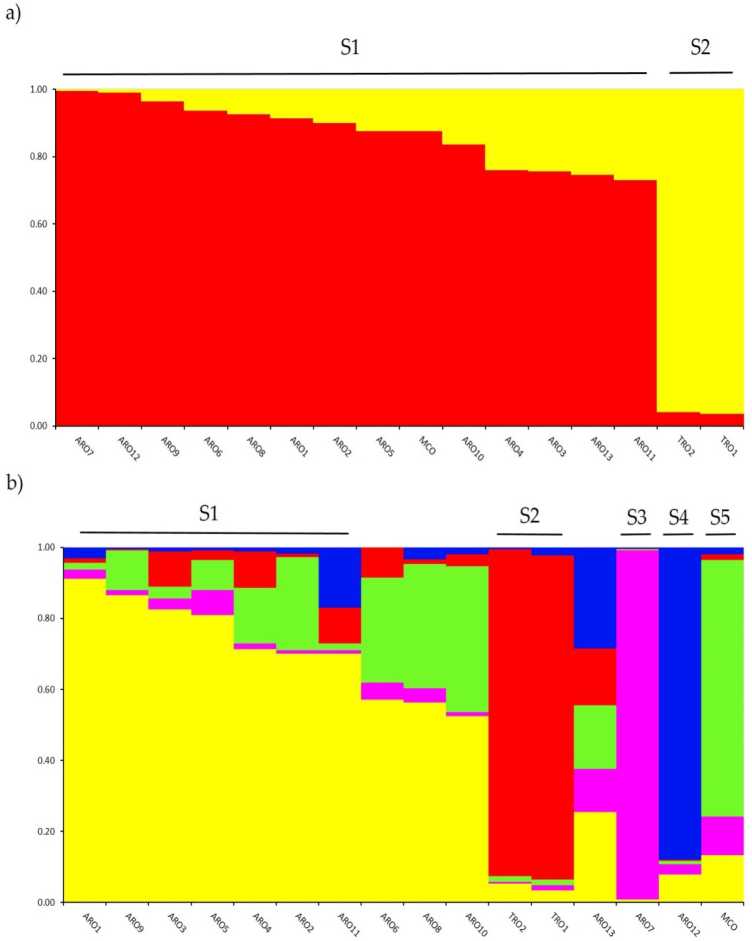
Relacions genètiques entre poblacions
El polimorfisme SSR va permetre dibuixar un dendrograma de la diversitat genètica i els resultats de l'anàlisi filogenètica es mostren a la figura 3a. Aquí, la col·lecció de germoplasma es va dividir en cinc grups fortament recolzats pels valors bootstrap. Les poblacions ARO7 i ARO12 es van separar immediatament de les poblacions restants i van formar dos grups diferents. El tercer clúster incloïa les dues poblacions comercials de TRO, mentre que el quart node dividia MCO d'onze poblacions ARO. La relació genètica que es produeix entre les poblacions es va investigar més a fons mitjançant l'anàlisi de coordenades principals (PCoA) (figura 3b). Com s'ha destacat anteriorment, les poblacions ARO es van agrupar fortament, excepte ARO12 i ARO7, que van aparèixer en posicions aïllades a la trama PCoA. Les dues poblacions TRO i MCO es van dispersar al panell inferior dret de la trama.
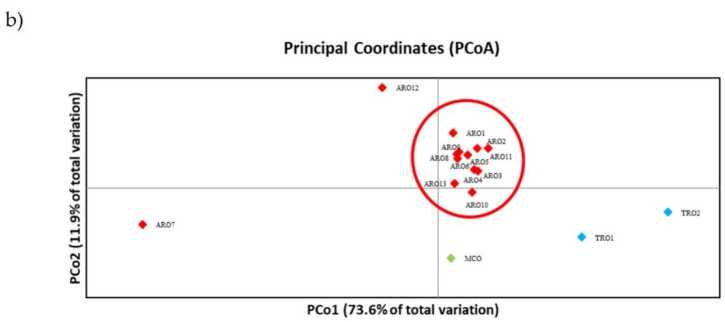
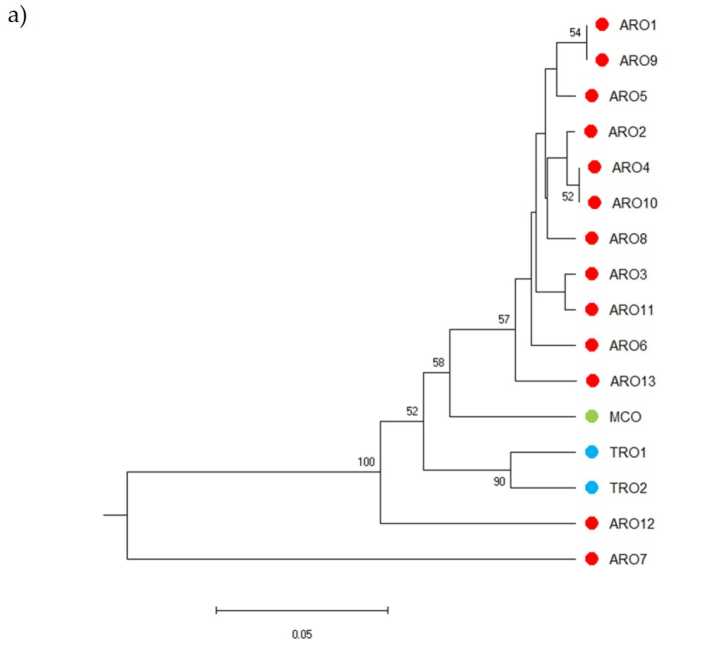
Figura 3. Diversitat genètica entre 16 A. cepa poblacions caracteritzades en aquest estudi, en funció del seu perfil SSR. (a) Dendrograma UPGMA de distància genètica. Els valors de suport d'arrencada >50 s'indiquen a sobre dels nodes corresponents; (b) anàlisi de components principals (PCoA). El clúster encerclat en vermell coincideix completament amb el grup generat per anàlisi filogenètica i constituït per 11 accessions ARO.
Discussion
Dins de la gran quantitat d'agrobiodiversitat conreada tradicionalment al sud d'Itàlia, les varietats locals de ceba representen productes de nínxol que cal preservar del risc d'erosió genètica i de l'amenaça de substitució per cultivars moderns. En el marc del projecte regional BiodiverSO, amb l'objectiu de recollir, caracteritzar, promoure i salvaguardar els recursos genètics de la regió de Puglia fortament vinculats al patrimoni local, vam establir una col·lecció de llavors de 13 poblacions de la raça local ARO. Es va informar de la primera avaluació de la variació d'ARO en termes de polimorfismes d'ADN i dos paràmetres bioquímics, continguts de sòlids solubles i àcid pirúvic, relacionats amb els trets de sabor i d'importància per a l'acceptació dels productes frescos sense cuinar. A més, es van comparar les dades sobre la varietat autòctona ARO amb les recollides en altres dues varietats locals de ceba pigmentada amb les quals sovint s'equivocava.
Les anàlisis bioquímiques van posar de manifest la dolçor de les 13 poblacions d'ARO, relacionada amb un alt contingut de sòlids solubles i una picor mitjana, segons les directrius de la indústria de la ceba dolça. [31]. Les bombetes ARO eren més dolces que les de les races locals TRO i MCO i mostraven una picant lleugerament més alta. No obstant això, la dolçor de les cebes es deu a un equilibri entre el contingut de sucre i la picor, per tant aquesta caracterització podria ser útil per donar suport a la selecció de genotips de valor, normalment realitzada pels agricultors només en funció de la morfologia.
Es va confirmar que els marcadors SSR eren una eina útil per discriminar genotips, tot i que recollits dins d'una zona de creixement estreta com la ciutat d'Acquaviva delle Fonti. Els marcadors seleccionats mostraven un nombre més gran d'al·lels que els marcadors que havien informat anteriorment [43] i [44], però inferior als marcadors informats per [45]. A més, el 50% del nostre conjunt de marcadors va mostrar valors d'índex PIC superiors a 0.5, demostrant ser adequats per discriminar les poblacions de la col·lecció, tal com suggereix [46]. L'avaluació de la diversitat dins de les poblacions va revelar valors similars entre Ho i He, donant lloc a un baix Fis valors. Això està d'acord amb la naturalesa d'encreuament exterior de A. cepa, que pateix greument depressió endogàmica [47]. El conjunt de Fis el valor calculat a les poblacions de ceba considerades en aquest estudi (0.054) va ser inferior a l'informat anteriorment per [45] (0.22) i gairebé idèntica a la trobada per [31] (0.08) i [48] (0.00) que van avaluar la diversitat genètica en races locals de ceba del nord-oest d'Espanya i del Níger, respectivament. Els nivells notables d'heterozigositat a les poblacions d'ARO reforcen la idea que Apulia representa un centre de diversitat per a moltes espècies hortícoles. [32, 42, 49-51].
AMOVA va destacar que la major part de la variació molecular de la col·lecció genotipada en aquest estudi es troba dins de les poblacions. No obstant això, una diferenciació genètica significativa entre les poblacions (FPT valors) van revelar l'aparició d'estratificació genètica. De fet, tot i que els nostres resultats van indicar la presència d'uniformitat genètica a la majoria de poblacions ARO, formant un clúster ben definit, les poblacions ARO7 i ARO12 mostraven un perfil genètic clarament diferent. Aquest resultat podria ser degut a un origen diferent de les llavors utilitzades pels dos pagesos dels quals es van recollir les poblacions. A més, a partir dels resultats obtinguts, la raça local ARO es pot considerar clarament diferent a nivell genètic de les races locals TRO i MCO. En un estudi recent, [29] va avaluar la diversitat genètica de diverses races de ceba italianes, com ara "Acquaviva", "Tropea" i "Montoro". Tot i que els autors van utilitzar marcadors SNP per avaluar la diversitat genètica d'una col·lecció de ceba més àmplia, el genotipat no va poder discriminar "Acquaviva" de les cebes "Tropea" i "Montoro". Probablement, aquesta discrepància es deu al baix valor PIC mitjà trobat (0.292), cosa que suggereix una informació general modesta dels loci analitzats, tal com afirma. [29]. A més, per investigar la presència de subestructura en el seu clúster italià, hauria estat millor analitzar els genotips italians per separat de la resta de la col·lecció. Probablement hauria permès visualitzar un patró de diversitat genètica vinculat a l'estratificació geogràfica o trets sota selecció empírica.
En conclusió, el present estudi representa un informe complet sobre una varietat de ceba associada al patrimoni cultural local i d'importància econòmica per als agricultors. Els nostres resultats posen de manifest que, amb poques excepcions, ARO es caracteritza per un conjunt de gens ben definit, que mereix ser preservat del risc d'erosió genètica. Per tant, l'establiment d'una col·lecció representativa d'aquesta valuosa font de diversitat genètica ha estat crucial. Finalment, la caracterització genètica i fenotípica d'ARO podria ser útil per obtenir marques de qualitat de la Unió Europea.
Materials i mètodes
Recollida de germoplasma, material vegetal i extracció d'ADN
Es va adquirir un conjunt de 13 poblacions de la raça local ARO en el marc d'un projecte de la regió de Puglia (BiodiverSO: https://www.biodiversitapuglia.it/), a través d'una sèrie de missions realitzades a “Acquaviva delle Fonti”, una petita localitat de Puglia a la província de Bari, Itàlia. Els llocs de recollida de cada accessions es van cartografiar mitjançant el Sistema d'Informació Geogràfica (GIS) i es van informar a la taula 4. A més, en el present estudi es van incloure dues poblacions de la raça local TRO i una població de la raça local MCO i es van utilitzar com a referències. Tot el material vegetal es va cultivar en les mateixes condicions ambientals a la granja experimental “P Martucci” de la Universitat de Bari (41° 1'22.08″ N, 16°54'25.95″ E), sota gàbia de protecció per evitar la pol·linització creuada entre poblacions i assegurant la pol·linització intrapoblacional mitjançant mosques blaugrana (Lucília caesar). Les 16 poblacions es van caracteritzar per trets relacionats amb la mida i la forma del bulb i el color de la pell i la carn (taula S1). A més, es va realitzar un assaig de contingut sòlid soluble mitjançant un refractòmetre de mà i es va mesurar la picor en mostres de suc de ceba afegint 2,4-dinitrofenil hidrazina (0.125% v/v en 2N d'HCl) i avaluant l'absorbància a 420 nm, tal com informa [31]. La prova de rang múltiple de Duncan i la prova SNK es van dur a terme per determinar la presència de diferències significatives.
Taula 4. Llista de poblacions recollides i genotipades en aquest estudi. Per a cada població, s'informa el codi d'identificació, el nom local, la coordenada GPS i el banc de gens que preserva les llavors.
| codi | Nom | Coordenades GPS | Banc de gens y |
| ARO1 | Cipolla rossa di Acquaviva | 40°54’21.708″ N 16°49’1.631” E | Di.SSPA |
| ARO2 | Cipolla rossa di Acquaviva | 40°53’14.28″ N 16°48’56.879” E | Di.SSPA |
| ARO3 | Cipolla rossa di Acquaviva | 40°54’11.304″ N 16°49’13.079” E | Di.SSPA |
| ARO4 | Cipolla rossa di Acquaviva | 40°54’3.348″ N 16°40’27.011” E | Di.SSPA |
| ARO5 | Cipolla rossa di Acquaviva | 40°51’59.76″ N 16°53’0.527” E | Di.SSPA |
| ARO6 | Cipolla rossa di Acquaviva | 40°52’48.72″ N 16°49’43.247” E | Di.SSPA |
| ARO7 | Cipolla rossa di Acquaviva | 40°53’13.47″ N 16°50’23.783” E | Di.SSPA |
| ARO8 | Cipolla rossa di Acquaviva | 40°53’18.816″ N 16°49’33.888” E | Di.SSPA |
| ARO9 | Cipolla rossa di Acquaviva | 40°54'51.372 ″ N 16°49'3.504" E | Di.SSPA |
| ARO10 | Cipolla rossa di Acquaviva | 40°54’1.188″ N 16°49’24.311” E | Di.SSPA |
| ARO11 | Cipolla rossa di Acquaviva | 40°52'49.8 ″ N 16°49'48.575" E | Di.SSPA |
| ARO12 | Cipolla rossa di Acquaviva | 40°52’38.892″ N 16°49’28.379” E | Di.SSPA |
| ARO13 | Cipolla rossa di Acquaviva | 40°53’21.768″ N 16°49’29.711” E | Di.SSPA |
| TRO1 | Cipolla rossa llarga de Tropea | - | Di.SSPA |
| TRO2 | Cipolla rossa tonda di Tropea | - | Di.SSPA |
| MCO | Cipolla ramata di Montoro | - | Di.SSPA |
| y Di.SSPA, Departament de Ciències del Sòl, Plantes i Aliments, Universitat de Bari. |
Es va mostrejar material de fulles de 20 genotips per població i es va emmagatzemar a -80 ° C fins al seu ús. Per a espècies riques en polisacàrids, com A. cepa, Els primers passos per eliminar els polisacàrids són essencials per obtenir ADN de bona qualitat, per tant, els rentats inicials en tampó STE (sacarosa 0.25, 0.03 M, Tris 0.05, XNUMX M, EDTA XNUMX, XNUMX M) es van realitzar tal com es descriu per [52]. L'ADN total es va extreure seguint el mètode CTAB [53] i finalment es va comprovar la qualitat i la concentració mitjançant l'espectrofotòmetre UV-vis Nano Drop 2000 (ThermoScientific, Waltham, MA, EUA) i electroforesi en gel d'agarosa al 0.8%.
Anàlisi SSR
16 combinacions d'imprimació EST-SSR desenvolupades per [54] i prèviament provat en estudis de diversitat genètica per [43] i [44] i 21 SSR genòmics [45-55] es van examinar per avaluar-ne la idoneïtat (taula complementària S4). El genotipat es va realitzar mitjançant el mètode d'etiquetatge fluorescent econòmic en què s'afegeix la cua M13 a cada imprimació SSR avançada. [56]. Les barreges de PCR es van preparar en una reacció de 20 gL que contenia: 50 ng d'ADN total, 0.2 mM de barreja dNTP, 1X de tampó de reacció PCR, 0.8 U d'ADN polimerasa DreamTaq (Thermo Scientific, Waltham, MA, EUA), 0.16 gM d'imprimació inversa , 0.032 gM d'imprimació directa estesa amb la seqüència M13 (5′-TGTAAAACGACGGCCAGT-3′) i 0.08 gM d'un imprimador M13 universal marcat amb colorants fluorescents FAM o NED (Sigma-Aldrich, St. Louis, MO, EUA). Les reaccions de PCR es van dur a terme al termociclador SimpliAmp (Applied Biosystems, CA, EUA) amb les condicions següents per a la majoria dels parells d'imprimació: 94 °C durant 5 min, 40 cicles a 94 °C durant 30 s, 58 °C durant 45 s i 72 °C durant 45 s i un allargament final a 72 °C durant 5 min. Pel que fa a ACM446 i ACM449, es va aplicar una PCR de touchdown amb recuit de 60 ° C a 55 ° C durant 10 cicles, 30 cicles a 55 ° C, seguit d'una extensió final de 5 min a 72 ° C. Els productes de PCR es van carregar en una placa de 96 pous i es van barrejar amb 14 gL de formamida Hi-Di (Life Technologies, Carlsbad, CA, EUA) i 0.5 gL GeneScan 500 ROX Size Standard (Life Technologies, Carlsbad, CA, EUA). Els amplicons es van resoldre mitjançant la màquina de seqüenciació capil·lar ABI PRISM 3100 Avant Genetic Analyzer (Life Technologies, Carlsbad, CA, EUA), on els al·lels es van puntuar com a codominants i es van assignar mitjançant la versió 3.7 del programari GeneMapper.
El programari GenAlEx 6.5 [57] i Cervus 3.0.7 [58] es van utilitzar per estimar el nombre d'al·lels (Na), el nombre d'al·lels efectius (Ne), l'heterozigositat observada (Ho), l'heterozigositat esperada (He), el contingut d'informació polimòrfica (PIC), l'índex d'informació de Shannon (I) i l'índex de fixació (Fis). ) per a cada locus SSR.
Avaluació de la diversitat genètica
GenAlEx 6.5 va avaluar la partició jeràrquica de la variació genètica entre i dins de les poblacions de ceba. [57] mitjançant l'anàlisi de la variància molecular (AMOVA) amb 999 bootstrapping per provar la importància. A més, es va utilitzar el programari GenAlEx 6.5 per estimar la diversitat dins de cada població calculant la mitjana de Ho, He i Fis sobre tots els loci SSR.
L'estructura de la població es va inferir per l'algoritme de agrupació basat en models bayesians implementat al programari STRUCTURE v.2.3.4. [59]. El conjunt de dades es va executar amb una sèrie de grups hipotètics (K), que van d'1 a 10, establint deu execucions independents per cada valor de K. Per a cada execució, amb l'objectiu de verificar la consistència dels resultats, es van realitzar 100,000 períodes de gravació inicial i 100,000 iteracions de Markov Chain Monte Carlo (MCMC) sota el model de barreja i freqüències d'al·lels independents entre les poblacions. El valor K més probable es va determinar implementant el mètode AK, descrit per [60], al programa web STRUCTURE HARVESTER [61]. Es va assignar una població individual a un clúster específic quan el seu coeficient de pertinença (valor q) era superior a 0.7, en cas contrari es considerava d'ascendència mixta.
Es va realitzar una anàlisi de coordenades principals per visualitzar els patrons de relació genètica entre les accessions revelats per la matriu de distància genètica de Nei (taula suplementària S5). A partir de les freqüències d'al·lel, es va construir un dendrograma de distància genètica implementant el mètode de grups de parells no ponderats amb anàlisi de clúster de mitjanes aritmètiques (UPGMA) al programari POPTREEW. [62]. Es va aplicar el bootstrapping per avaluar la confiança en la agrupació jeràrquica, establint 100 mostreigs del conjunt de dades. Finalment, el programari MEGA X [63] es va utilitzar com a programari de dibuix d'arbres.
Materials complementaris: Els següents estan disponibles en línia a http://www.mdpi.com/2223-7747/9/2/260/s1. Taula S1: Caracterització morfològica dels bulbs ARO, MCO i TRO. Taula S2: índexs d'heterozigositat i fixació calculats per a les races locals ARO i les races locals TRO i MCO. Taula S3: Valors per parelles del paràmetre Fpt. Taula S4: Llista dels SSR utilitzats en l'estudi. Taula S5. Matriu de població per parelles de la distància genètica de Nei. Figura S1: Gràfic de línies de valors K que canvien amb el Delta K d'Evanno.
Contribucions de l'autor: CL i LR van concebre l'estudi i van dissenyar l'experiment; CL i PI van realitzar anàlisis de marcadors moleculars; ARM i VZ van realitzar les proves de camp; RM, SP, GR i CL van participar en l'anàlisi de dades; RM i CL van escriure el manuscrit. Tots els autors han llegit i acceptat la versió publicada del manuscrit.
Finançament: Aquest treball va ser finançat pel projecte regional d'Apulia "Biodiversitat d'espècies vegetals d'Apulia"—Programma di Sviluppo Rurale per la Puglia 2014-2020. Misura 10—Sottomisura 10.2; beca CUP H92C15000270002, Itàlia.
Agraïments: Els agraïments es deuen a "Azienda Agricola Iannone Anna" i "Associazione produttori della vera cipolla rossa di Acquaviva" per proporcionar materials vegetals utilitzats en l'experiment.
Conflictes d'interès: Els autors declaren cap conflicte d'interès.
referències
- 1. Stearn, WT Quantes espècies d'Allium es coneixen? Kew Mag. 1992, 9, 180-182. [CrossRef]
- 2. FAOSTAT. Base de dades estadística de la FAO. Disponible en línia: http://www.fao.org/2017 (consultat el 8 de gener de 2019).
- 3. Block, E. La química de l'all i la ceba. Sci. Am. 1985, 252, 114-119. [CrossRef]
- 4. Lee, B.; Jung, JH; Kim, HS Avaluació de la ceba vermella sobre l'activitat antioxidant en rata. Química dels Aliments. Toxicol. 2012, 50, 3912, 3919. [CrossRef]
- 5. Lee, SM; Lluna, J.; Chung, JH; Cha, YJ; Shin, MJ Efecte dels extractes de pell de ceba rics en quercetina sobre la trombosi arterial en rates. Química dels Aliments. Toxicol. 2013, 57, 99, 105. [CrossRef] [PubMed]
- 6. Yoshinari, O.; Shiojima, Y.; Igarashi, K. Efectes anti-obesitat de l'extracte de ceba en rates grasses diabétiques de zucker. nutrients 2012, 4,1518-1526. [CrossRef]
- 7. Akash, MSH; Rehman, K.; Chen, S. Planta d'espècies Allium cepa: suplement dietètic per al tractament de la diabetis mellitus tipus 2. Nutrició 2014, 30, 1128-1137. [CrossRef] [PubMed]
- 8. Wang, Y.; Tian, WX; Ma, XF Efectes inhibidors de la ceba (Allium cepa L.) extracte sobre la proliferació de cèl·lules canceroses i adipòcits mitjançant la inhibició de la sintasa d'àcids grassos. Pac asiàtic. J. Càncer Prev. 2012,13, 5573, 5579. [CrossRef] [PubMed]
- 9. Lai, WW; Hsu, SC; Chueh, FS; Chen, YY; Yang, JS; Lin, JP; Lien, JC; Tsai, CH; Chung, JG La quercetina inhibeix la migració i la invasió de les cèl·lules canceroses orals humanes SAS mitjançant la inhibició de les vies de senyalització NF-kappaB i la metaloproteinasa de matriu-2/-9. Res. anticancerígena 2013, 33, 1941-1950. [PubMed]
- 10. Nicastro, HL; Ross, SA; Milner, JA All i cebes: les seves propietats de prevenció del càncer. Càncer Prev. Res. 2015, 8,181-189. [CrossRef]
- 11. Forte, L.; Torricelli, P.; Boanini, E.; Gazzano, M.; Rubini, K.; Fini, M.; Bigi, A. Propietats antioxidants i reparadores òssies de la hidroxiapatita funcionalitzada amb quercetina: un estudi in vitro de co-cultiu de cèl·lules endotelials-osteoblasts-osteoclasts. Acta Biomater. 2016, 32, 298, 308. [CrossRef]
- 12. Yamazaki, Y.; Iwasaki, K.; Mikami, M.; Yagihashi, A. Distribució d'onze precursors de sabor, derivats de S-Alk(en)il-L-cisteïna, en set verdures Allium. Ciència de l'alimentació. Tecnol. Res. 2011, 17, 55, 62. [CrossRef]
- 13. Block, E. La química organosulfurada del gènere Allium—Implicacions per a la química orgànica del sofre. Angew. Chem. Int. Ed. Anglès. 1992, 31, 1135-1178. [CrossRef]
- 14. Griffiths, G.; Trueman, L.; Crowther, T.; Tomàs, B.; Smith, B. Cebes-Un benefici global per a la salut. Phytother. Res. 2002,16, 603, 615. [CrossRef]
- 15. Schwimmer, S.; Weston, WJ Desenvolupament enzimàtic de l'àcid pirúvic a la ceba com a mesura de picor. J. Agric. Química dels Aliments. 1961, 9, 301, 304. [CrossRef]
- 16. Ketter, CAT; Randle, WM Avaluació de la picor a les cebes. En Estudis provats per a la docència de laboratori; Karcher, SJ, Ed.; Association for Biology Laboratory Education (ABLE): Nova York, NY, EUA, 1998; Volum 19, pàgs. 177-196.
- 17. Hanelt, P Taxonomia, evolució i història. En Cebes i cultius afins, vol. I. Botànica, Fisiologia i Genètica; Rabinowitch, HD, Brewster, JL, Eds.; CRC Press: Boca Raton, FL, EUA, 1990; pàgines 1-26.
- 18. Rabinowitch, HD; Currah, L. Allium Crop Science: Recent Advances; CABI Publishing: Wallingford, Regne Unit, 2002.
- 19. Mallor, C.; Carravedo, M.; Estopanan, G.; Mallor, F. Caracterització dels recursos genètics de la ceba (Allium cepa L.) de secundària espanyola centre de diversitat. Envergadura. J. Agric. Res. 2011, 9, 144-155. [CrossRef]
- 20. Ferioli, F.; D'Antuono, LF Avaluació de fenòlics i sulfòxids de cisteïna en germoplasma local de ceba i escalunya d'Itàlia i Ucraïna. Genet. Recurs. Crop Evol. 2016, 63, 601, 614. [CrossRef]
- 21. Petropoulos, SA; Fernandes, A.; Barros, L.; Ferreira, ICFR; Ntatsi, G. Descripció morfològica, nutricional i química de 'vatikiotiko', una varietat local de ceba de Grècia. Química Alimentària. 2015,182, 156-163. [CrossRef]
- 22. Liguori, L.; Adiletta, G.; Nazzaro, F.; Fratianni, F.; Di Matteo, M.; Albanese, D. Propietats bioquímiques, antioxidants i activitat antimicrobiana de diferents varietats de ceba a l'àrea mediterrània. J. Food Meas. Personatge. 2019,13, 1232-1241. [CrossRef]
- 23. Yoo, KS; Pike, L.; Crosby, K.; Jones, R.; Leskovar, D. Diferències en la picor de la ceba a causa dels conreus, l'entorn de creixement i la mida del bulb. Ciència. Hortic. 2006,110, 144-149. [CrossRef]
- 24. Beesk, N.; Perner, H.; Schwarz, D.; Jordi, E.; Kroh, LW; Rohn, S. Distribució de quercetina-3, 4′-O-diglucòsid, quercetina-4′-O-monoglucòsid i quercetina en diferents parts del bulb de ceba (Allium cepa L.) influenciada pel genotip. Química Alimentària. 2010,122, 566, 571. [CrossRef]
- 25. Caruso, G.; Conti, S.; Villari, G.; Borrelli, C.; Melchionna, G.; Minutolo, M.; Russo, G.; Amalfitano, C. Efectes del temps de trasplantament i la densitat de la planta sobre el rendiment, la qualitat i el contingut antioxidant de la ceba (Allium cepa L.) al sud d'Itàlia. Ciència. Hortic. 2014,166, 111-120. [CrossRef]
- 26. Pérez-Gregorio, MR; Regueiro, J.; Simal-Gandara, J.; Rodrigues, AS; Almeida, DPF Augment del valor afegit de la ceba com a font de flavonoides antioxidants: una revisió crítica. Crit. Rev. Food Sci. Nutr. 2014, 54,1050-1062. [CrossRef] [PubMed]
- 27. Pohnl, T.; Schweigert, RM; Carle, R. Impacte del mètode de cultiu i la selecció de conreus sobre els carbohidrats solubles i els principis picants de les cebes (Allium cepa L.). J. Agric. Química dels Aliments. 2018, 66, 12827-12835. [CrossRef] [PubMed]
- 28. Tedesco, I.; Carbone, V.; Spagnuolo, C.; Minasi, P.; Russo, GL Identificació i quantificació de flavonoides de dos cultivars del sud d'Itàlia Allium cepa L., Tropea (ceba vermella) i Montoro (ceba de coure), i la seva capacitat per protegir els eritròcits humans de l'estrès oxidatiu. J. Agric. Química dels Aliments. 2015, 63, 5229, 5238. [CrossRef]
- 29. Villano, C.; Esposito, S.; Carucci, F.; Frusciante, L.; Carputo, D.; Aversano, R. El genotipat d'alt rendiment a la ceba revela l'estructura de la diversitat genètica i els SNP informatius útils per a la reproducció molecular. Mol. Raça. 2019, 39, 5. [CrossRef]
- 30. Mercati, F.; Longo, C.; Poma, D.; Araniti, F.; Lupini, A.; Mammano, MM; Fiore, MC; Abenavoli, MR; Sunseri, F Variació genètica d'un tomàquet italià de llarga vida útil (Solanum lycopersicum L.) recollida mitjançant SSR i trets morfològics del fruit. Genet. Recurs. Crop Evol. 2014, 62, 721, 732. [CrossRef]
- 31. González-Pérez, S.; Mallor, C.; Garces-Claver, A.; Merino, F.; Taboada, A.; Rivera, A.; Pomar, F.; Perovic, D.; Silvar, C. Explorant la diversitat genètica i els trets de qualitat en una col·lecció de ceba (Allium cepa L.) races autòctones del nord-oest d'Espanya. Genètica 2015, 47, 885, 900. [CrossRef]
- 32. Lotti, C.; Iovieno, P.; Centomani, I.; Marcotrigiano, AR; Fanelli, V.; Mimiola, G.; Summo, C.; Pavan, S.; Ricciardi, L. Caracterització genètica, bioagronòmica i nutricional de la kale (Brassica oleracea L. var. acèfala) diversitat a Apulia, sud d'Itàlia. Diversitat 2018,10, 25. [CrossRef]
- 33. Bardaro, N.; Marcotrigiano, AR; Bracuto, V.; Mazzeo, R.; Ricciardi, F.; Lotti, C.; Pavan, S.; Ricciardi, L. Anàlisi genètica de la resistència a Orobanche crenata (Forquilla.) en un pèsol (Pisum sativum L.) línia de baixa estrigolactona. J. Plant Pathol. 2016, 98, 671-675.
- 34. Wako, T.; Tsukazaki, H.; Yaguchi, S.; Yamashita, K.; Ito, S.; Shigyo, M. Mapeig de loci de trets quantitatius per al temps d'embolcall en ceba agrupada (Allium fistulosum L.). Euphytica 2016, 209, 537, 546. [CrossRef]
- 35. Dhaka, N.; Mukhopadhyay, A.; Paritosh, K.; Gupta, V.; Pental, D.; Pradhan, AK Identificació de SSR genètiques i construcció d'un mapa d'enllaç basat en SSR Brassica juncea. Euphytica 2017, 213, 15. [CrossRef]
- 36. Anandhan, S.; Mote, SR; Gopal, J. Avaluació de la identitat varietal de ceba mitjançant marcadors SSR. Seed Sci. Tecnol. 2014, 42, 279, 285. [CrossRef]
- 37. Mitrova, K.; Svoboda, P.; Ovesna, J. La selecció i validació d'un conjunt de marcadors per a la diferenciació de cultivars de ceba de la República Txeca. Txec J. Genet. Raça Vegetal. 2015, 51, 62, 67. [CrossRef]
- 38. Di Rienzo, V.; Miazzi, MM; Fanelli, V.; Sabetta, W.; Montemurro, C. La preservació i caracterització de la biodiversitat del germoplasma de l'olivera d'Apulia. Acta Hortic. 2018,1199,1-6. [CrossRef]
- 39. Mallor, C.; Arnedo-Andrés, A.; Garces-Claver, A. Avaluar la diversitat genètica del castellà Allium cepa races locals per a la cria de ceba utilitzant marcadors microsatèl·lits. Ciència. Hortic. 2014,170, 24-31. [CrossRef]
- 40. Rivera, A.; Mallor, C.; Garcés-Claver, A.; Garcia-Ulloa, A.; Pomar, F.; Silvar, C. Avaluació de la diversitat genètica en ceba (Allium cepa L.) races autòctones del nord-oest d'Espanya i comparació amb la variabilitat europea. NZJ Crop Hortic. 2016, 44, 103-120. [CrossRef]
- 41. De Giovanni, C.; Pavan, S.; Taranto, F.; Di Rienzo, V.; Miazzi, MM; Marcotrigiano, AR; Mangini, G.; Montemurro, C.; Ricciardi, L.; Lotti, C. Variació genètica d'una col·lecció global de germoplasma de cigrons (Cicer arietinum L.) incloses les accessions italianes amb risc d'erosió genètica. Physiol. Mol. Biol. Plantes 2017, 23, 197-205. [CrossRef]
- 42. Mazzeo, R.; Morgese, A.; Sonnante, G.; Zuluaga, DL; Pavan, S.; Ricciardi, L.; Lotti, C. Genetic diversity in bròquil rabe (Brassica rapa L. subsp. sylvestris (L.) Janch.) del sud d'Itàlia. Ciència. Hortic. 2019, 253, 140-146. [CrossRef]
- 43. Jakse, M.; Martín, W.; McCallum, J.; Havey, M. Polimorfismes d'un sol nucleòtid, indels i repeticions de seqüències simples per a la identificació de conreus de ceba. Melmelada. Soc. Hortic. Ciència. 2005,130, 912, 917. [CrossRef]
- 44. McCallum, J.; Thomson, S.; Pither-Joyce, M.; Kenel, F. Anàlisi de la diversitat genètica i desenvolupament de marcadors de polimorfisme d'un sol nucleòtid en ceba de bulb cultivada basat en marcadors de repetició de seqüència simple d'etiquetes de seqüència expressada. Melmelada. Soc. Hortic. Ciència. 2008,133, 810, 818. [CrossRef]
- 45. Baldwin, S.; Pither-Joyce, M.; Wright, K.; Chen, L.; McCallum, J. Desenvolupament de marcadors de repetició de seqüències simples genòmiques robustes per a l'estimació de la diversitat genètica dins i entre la ceba del bulb (Allium cepa L.) poblacions. Mol. Raça. 2012, 30, 1401-1411. [CrossRef]
- 46. DeWoody, JA; Honeycutt, RL; Skow, LC Marcadors de microsatèl·lits en cérvol de cua blanca. J. Hered. 1995, 86, 317-319. [CrossRef] [PubMed]
- 47. Khodadadi, M.; Hassanpanah, D. Ceba iraniana (Allium cepa L.) les respostes dels cultivars a la depressió de consanguinitat. Món aplicació. Ciència. J. 2010,11, 426, 428.
- 48. Abdou, R.; Bakasso, Y.; Saadou, M.; Baudoin, JP; Hardy, OJ Diversitat genètica de cebes del Níger (Allium cepa L.) avaluat mitjançant marcadors de repetició de seqüència simple (SSR). Acta Hortic. 2016,1143, 77-90. [CrossRef]
- 49. Pavan, S.; Lotti, C.; Marcotrigiano, AR; Mazzeo, R.; Bardaro, N.; Bracuto, V.; Ricciardi, F.; Taranto, F.; D'Agostino, N.; Schiavulli, A.; et al. Un grup genètic diferent en cigrons conreats, tal com es va revelar pel descobriment i el genotipat de marcadors a tot el genoma. Genoma vegetal 2017, 2017,10. [CrossRef]
- 50. Pavan, S.; Marcotrigiano, AR; Ciani, E.; Mazzeo, R.; Zonno, V.; Ruggieri, V.; Lotti, C.; Ricciardi, L. Genotipatge per seqüenciació d'un meló (Cucumis melo L.) la col·lecció de germoplasma d'un centre secundari de diversitat destaca els patrons de variació genètica i les característiques genòmiques de diferents pools de gens. BMC Genom. 2017, 18, 59. [CrossRef]
- 51. Di Rienzo, V.; Sió, S.; Taranto, F.; D'Agostino, N.; Montemurro, C.; Fanelli, V.; Sabetta, W.; Boucheffa, S.; Tamendjari, A.; Pasqualone, A.; et al. Flux genètic entre les poblacions d'olivera a la conca mediterrània. Peer J. 2018, 6. [CrossRef]
- 52. Pastor, LD; McLay, TG Dos protocols a microescala per a l'aïllament d'ADN del teixit vegetal ric en polisacàrids. J. Plant Res. 2011,124, 311, 314. [CrossRef]
- 53. Doyle, JJ; Doyle, JL Aïllament d'ADN vegetal a partir de teixit fresc. Enfocar 1990,12, 13-14.
- 54. Kuhl, JC; Cheung, F.; Qiaoping, Y.; Martín, W.; Zewdie, Y.; McCallum, J.; Catanach, A.; Rutherford, P.; Aigüera, KC; Jenderek, M.; et al. Un conjunt únic d'11,008 etiquetes de seqüència expressada de ceba revela diferències de seqüència expressada i genòmiques entre els ordres monocot asparagales i poales. Cèl·lula vegetal 2004,16, 114, 125. [CrossRef]
- 55. Kim, HJ; Lee, RRHH; Hyun, JY; Cançó, KH; Kim, KH; Kim, JE; Hur, CG; Harn, desenvolupament de marcadors CH per a proves de puresa genètica de ceba mitjançant SSR Finder. Corea J. Raça. Ciència. 2012, 44, 421, 432. [CrossRef]
- 56. Schuelke, M. Un mètode econòmic per a l'etiquetatge fluorescent de fragments de PCR. Nat. Biotecnologia. 2000, 18, 233, 234. [CrossRef] [PubMed]
- 57. Peakall, R.; Smouse, PE GenAlEx 6.5: Anàlisi genètica en Excel. Programari genètic de poblacions per a la docència i la recerca: una actualització. bioinformàtica 2012, 28, 2537, 2539. [CrossRef] [PubMed]
- 58. Kalinowski, ST; Taper, ML; Marshall, TC La revisió de com el programa informàtic CERVUS s'adapta a l'error de genotipat augmenta l'èxit en l'assignació de paternitat. Mol. Ecol. 2007,16, 1099-1106. [CrossRef]
- 59. Pritchard, JK; Stephens, M.; Rosenberg, NA; Donnelly, P. Mapeig de l'associació en poblacions estructurades. Am. J. Hum. Genet. 2000, 67, 170-181. [CrossRef]
- 60. Evanno, G.; Regnaut, S.; Goudet, J. Detecting the number of clusters of individuals using the software ESTRUCTURE: A simulation study. Mol. Ecol. 2005,14, 2611, 2620. [CrossRef]
- 61. Earl, D.; VonHoldt, B. STRUCTURE HARVESTER: Un lloc web i un programa per visualitzar la sortida d'STRUCTURE i implementar el mètode d'Evanno. Conserv. Genet. Recurs. 2011, 4. [CrossRef]
- 62. Takezaki, N.; Nei, M.; Tamura, K. POPTREEW: versió web de POPTREE per construir arbres de població a partir de dades de freqüència d'al·lels i calcular algunes altres quantitats. Mol. Biol. Evol. 2014, 31, 1622-1624. [CrossRef]
- 63. Kumar, S.; Stecher, G.; Li, M.; Knyaz, C.; Tamura, K. MEGA X. Molecular Evolutionary Genetics Analysis through computing platforms. Mol. Biol. Evol. 2018, 35, 1547-1549. [CrossRef]